本教程涵盖了如何使用FreeSurfer与MNE-Python一起,来处理我们用于构建头皮、内/外颅骨和皮质表面的受试特异的解剖模型的结构项MRI数据。
FreeSurfer是一个MRI数据的开源分析工具箱,可从https://surfer.nmr.mgh.harvard.edu/获取。FreeSurfer提供了可视化MRI数据的图形界面、用于创建感兴趣区域ROI标签的几个解剖分区、模板大脑如fsaaverage,以及用于寻找组织边界或转换大脑以对齐不同受试的相似解剖区域等任务的几个命令行工具。
这些FreeSurfer功能对于MNE-Python计算正模型和建立相应的源空间(位于皮层表面或大脑体积内的磁偶极子网格)是极为必要的。
第一步
下载并安装FreeSurfer后,有几个步骤来设置环境。首先定义一个环境变量FREESURFER_HOME,运行:
1 | export FREESURFER_HOME=/path/to/FreeSurfer |
FreeSurfer的主目录会根据你的操作系统和安装时的选择而有所不同。更多信息请参阅FreeSurfer安装指南。
另一个重要的步骤是告诉FreeSurfer把你的研究对象的解剖重建放在哪里。这是通过一个名为SUBJECTS_DIR的环境变量完成的,它将在单独的子文件夹中包含各个主题的重建。
1 | export SUBJECTS_DIR=/path/to/your/subjects_dir |
解剖重建
第一个处理阶段是创建各种表面重建。通常,完整的FreeSurfer重构可以通过以下命令获得:
1 | my_subject=sample |
其中i代表input,s代表subject。执行此操作将创建文件夹$SUBJECTS_DIR/sample,并使用几个子文件夹(bem, label, mri等)填充它。
注意:即使在一个很快的计算机上,解剖重建也可能需要几个小时。
FreeSurfer执行半球分离,因此大多数结果文件有独立的左右半球版本,以前缀lh或rh表示。这种半球分离由mne-python(例如,mne.SourceEstimate)保存。SourceEstimate对象分别存储两个半球的空间位置(顶点);
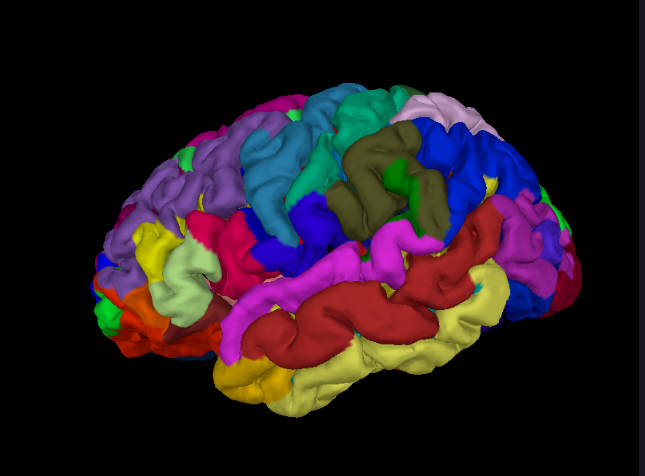
下面我们展示了样本数据集受试左半球的FreeSurfer重建结果的示例,包括解剖分区的覆盖。
1 | import mne |
结合MEN-Python
为了保证源定位分析的正常工作,FreeSurfer重构过程必须事先完成。此外,对于许多与逆成像相关的MNE-Python函数(如mne.setup_source_space), SUBJECTS_DIR必须全局定义(作为环境变量或通过调用mne.set_config),或在每次函数调用中通过传递关键字参数SUBJECTS_DIR ='/path/to/your/ SUBJECTS_DIR 单独指定。
有关MNE- python和FreeSurfer如何集成的更多细节,请参见接下来的教程。
‘fsaverage’
在安装期间,FreeSurfer将一个名为“fsaverage”的受试复制到$FREESURFER_HOME/subjects/ fsaaverage。fsaverage是一个模板大脑,基于40个真实大脑的核磁共振扫描的组合。fsaverage主题文件夹包含正常主题重构将产生的所有文件。有关用于创建fsaverage的主题的详细信息,请参见https://surfer.nmr.mgh.harvard.edu/fswiki/FsAverage获取概述,并参见https://surfer.nmr.mgh.harvard.edu/fswiki/Buckner40Notes。fsaverage的副本也作为示例数据集的一部分提供,也作为独立数据集分发。
fsaverage最常见的用途之一是作为皮质源估计转换的目标空间。换句话说,将每个个体受试者的估计大脑活动变化到fsaverage大脑是很常见的,这样就可以进行组级别的统计比较。